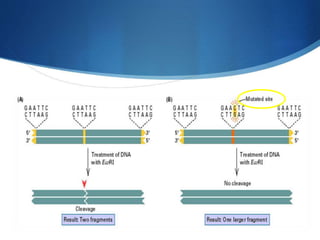
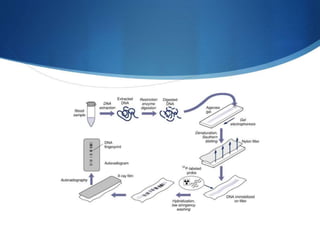
Il polimorfismo di lunghezza di frammento di restrizione (RFLP) è una tecnica genetica sviluppata nel 1984 per analizzare le variazioni nel DNA tra organismi. Utilizza l'estrazione e la digestione del DNA seguita da elettroforesi e analisi per identificare marcatori genetici, utile in diverse applicazioni come la paternità e medicina forense. Tuttavia, presenta limitazioni in termini di sensibilità e interpretazione, richiedendo quantità considerevoli di DNA e apparecchiature complesse.