Inmunidad en procariotas. Guía basada en la metodología POGIL.pdf
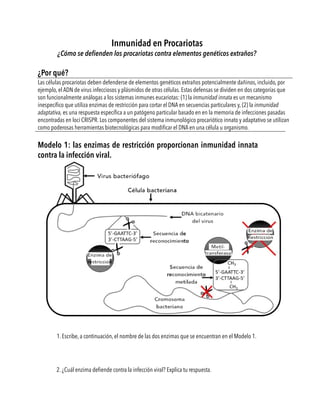
- 1. ¿Por qué? 1. Escribe, a continuación, el nombre de las dos enzimas que se encuentran en el Modelo 1. 2. ¿Cuál enzima defiende contra la infección viral? Explica tu respuesta. Inmunidad en Procariotas ¿Cómo se defienden los procariotas contra elementos genéticos extraños? Las células procariotas deben defenderse de elementos genéticos extraños potencialmente dañinos, incluido, por ejemplo, el ADN de virus infecciosos y plásmidos de otras células. Estas defensas se dividen en dos categorías que son funcionalmente análogas a los sistemas inmunes eucariotas: (1) la inmunidad innata es un mecanismo inespecífico que utiliza enzimas de restricción para cortar el DNA en secuencias particulares y, (2) la inmunidad adaptativa, es una respuesta específi ca a un patógeno particular basado en en la memoria de infecciones pasadas encontradas en loci CRISPR. Los componentes del sistema inmunológico procariótico innato y adaptativo se utilizan como poderosas herramientas biotecnológicas para modificar el DNA en una célula u organismo. Modelo 1: las enzimas de restricción proporcionan inmunidad innata contra la infección viral.
- 2. 2 4. Examina el mecanismo de defensa bacteriano ilustrado en el Modelo 1. 3. ¿Cuál enzima protege a la bacteria de su propio mecanismo de defensa? Explica tu respuesta. a. Individualmente, decide si este mecanismo de defensa es específico del virus. b. Compara la respuesta que diste a la parte "a" con las respuestas de los compañeros que integran tu grupo. ¿Todos llegaron a la misma conclusión? d. El examen de la evidencia enumerada en la parte "c" ¿permitió a tu grupo llegar a una respuesta de consenso a la pregunta de la parte "a"? e. ¿Qué información adicional permitiría a tu grupo llegar a una respuesta de consenso a la pregunta de la parte “a”, si no lo ha hecho? c. ¿Qué evidencia del Modelo 1 utilizaron los miembros individuales del grupo para tomar su decisión? 5. ¿Cuáles son las consecuencias para una célula bacteriana si la enzima metiltransferasa se inactiva por completo?
- 3. 3 . Antes del cambio Después del cambio b. Si la mutación puntual descrita en la parte “a” ocurriera en cada secuencia de reconocimiento de EcoRI en un genoma viral, ¿cómo se vería afectada la actividad de EcoRI? c. Si la mutación puntual descrita en la parte “a” ocurriera en cada secuencia de reconocimiento de EcoRI en un genoma viral, ¿podría una célula de E. coli defenderse contra ese virus? ¿Por qué o por qué no? 5’ -GAATTC- 3’ 3’ -CTTAAG- 5’ 5’ -GGATTC- 3’ 3’ -CCTAAG- 5’ a. Predice la consecuencia de esta mutación puntual sobre la actividad de EcoRI. 6. Las enzimas de restricción cortan el DNA en secuencias de reconocimiento específicas. En la bacteria Escherichia coli (E. coli), la enzima EcoRI corta la secuencia de reconocimiento 5’-GAATTC-3’ mostrada en el Modelo 1. Otras enzimas de restricción de E. coli cortan diferentes secuencias de reconocimiento. La siguiente mutación puntual (resaltada en rojo) ocurre en una secuencia de reconocimiento de EcoRI en un genoma viral:
- 4. 4 7. Para generar una memoria de infecciones pasadas, pequeños fragmentos de DNA extraño, llamados protoespaciadores, se integran en los cromosomas procarióticos en lugares (loci) llamados loci CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas). Una vez integrado en un locus CRISPR, el fragmento de DNA extraño de 30-50 pares de bases único se denomina DNA espaciador, que está fl anqueado por secuencias de DNA repetitivas cortas (20-50 pares de bases) llamadas repeticiones CRISPR. a) ¿Qué es un protoespaciador? c) ¿Qué secuencia es muy variable en un locus CRISPR? A. Repeticiones CRISPR B. Espaciadores b) ¿Qué complejo enzimático integra a un protoespaciador en el locus CRISPR? Modelo 2: pequeños fragmentos de ADN viral se integran en los loci CRISPR para formar un registro de infecciones pasadas.
- 5. 5 d) ¿Qué parte del locus CRISPR confiere a la célula un recuerdo de una infección viral pasada? B. Espaciadores A. repeticiones CRISPR. 8. Un virus bacteriófago inyecta su genoma de DNA en una célula bacteriana. ¿Cómo se fragmenta el genoma del bacteriófago para ser adquirido por la integrasa espaciadora? 9. La integrasa espaciadora es un complejo de proteínas 1 y 2 asociadas a CRISPR (Cas1 y Cas2) que insertan en el locus CRISPR secuencias protoespaciadoras adquiridas a partir de DNA extraño. Responde las siguientes preguntas individualmente y luego compara las respuestas con las de tus compañeros de equipo.A continuación, el registrador anotará las respuestas de consenso del equipo. a) ¿Cómo carga la integrasa espaciadora el DNA viral en el locus CRISPR, en vez de cargar el DNA del cromosoma bacteriano? b) ¿Por qué la integración de DNA bacteriano en un locus CRISPR por la integrasa espaciadora es peligrosa para una célula bacteriana? c) La integración del DNA viral en el locus CRISPR mediante la integrasa espaciadora, ¿protege directamente a la célula bacteriana de una infección viral? ¿Por qué o por qué no? d) La integración del DNA viral en el locus CRISPR mediante la integrasa espaciadora, ¿es una forma de inmunidad innata o adaptativa? Explica tu respuesta.
- 6. 6 Modelo 3: los loci CRISPR proporcionan a los procariotas una respuesta inmune adaptativa específica para un DNA objetivo.
- 7. 7 10. La respuesta inmune adaptativa procariota utiliza un dúplex de RNA, llamado RNA guía (gARN). Basándote en el modelo 3: a) ¿Cuáles son los dos componentes del dúplex de gRNA? d) ¿Qué espaciador (# 1, 2 ó 3) del locus CRISPR se usó para generar el crRNA? 11. Individualmente y de acuerdo con la respuesta de tu equipo a la pregunta nº 10, decide qué componente de gRNA es responsable de identificar el DNA extraño en la célula, ¿el crRNA? o tracrRNA?. a) Comparte tu respuesta con tus compañeros de equipo. ¿Llegaron todos a la misma conclusión? b) Después de la discusión, ¿alguien cambió su respuesta? c) Si corresponde, ¿qué información u observaciones del Modelo 3 llevaron a un cambio dada a la respuesta? b) ¿Qué componente del dúplex de gRNA es complementario al DNA del bacteriófago? Explica tu respuesta a continuación y rotula directamente el Modelo 3. c) ¿Cuál proceso se utilizó para sintetizar el componente CRISPR-RNA (crRNA) del gRNA?
- 8. 8 d) En equipo, decidan qué componente del dúplex de RNA es responsable de identificar el ADN extraño en la célula.A continuación, el registrador del equipo escribirá la respuesta de consenso y, finalmente deberá ser escrita en la guía, por cada uno de los integrantes. e) Discute la respuesta que diste a las preguntas 10 y 11 con tu facilitador o instructor, antes de pasar a la pregunta 12. 12. El dúplex de gRNA se forma cuando una región de tracrRNA se aparea con una región complementaria de crRNA. a) Identifica, directamente en el Modelo 3, la región de apareamiento de bases entre tracrRNA y crRNA. b) Hipotetiza la función de tracrRNA. c) ¿Qué experimento podrías realizar para probar tu hipótesis de la función del tracrRNA? d) Basándote en en tu hipótesis que formulaste a la parte "b", predice el resultado de tu experimento a) Una vez unido al tracrRNA, ¿qué acción realiza la nucleasa Cas9 sobre el DNA extraño a la célula? 13. El componente tracrRNA del gRNA es necesario para unirse a la enzima nucleasa Cas9 (proteína 9 asociada a CRISPR).A su vez, la nucleasa Cas9 actuará invadiendo el DNA.
- 9. 9 b) ¿Actúa la nucleasa Cas9 sobre el DNA diana específico o actúa sobre cualquier DNA, independientemente de su origen? Explica tu respuesta. 14. Describe qué aspectos de la inmunidad adaptativa procariota se alterarían si los siguientes componentes fallaran en una célula. tracrRNA RNA espaciador a) b) c) Nucleasa Cas9 (proteína 9 asociada a CRISPR) 15. Una célula de E. coli sobrevive a una infección viral causada por un bacteriófago e incorpora un pequeño fragmento de DNA viral en su locus CRISPR. Cuando esta célula se reproduce por fisión binaria, ¿reciben ambas células hijas este "recuerdo" de la infección viral? ¿Por qué o por qué no?
- 10. 10 Preguntas de profundización 16. Cuando una célula bacteriana es infectada por primera vez por un tipo particular de virus, ¿la nucleasa Cas9 se dirige hacia el DNA viral? ¿Por qué o por qué no? 17. La edición del genoma implica la modificación artificial del DNA en células vivas o en un organismo. Las diferentes estrategias de edición del genoma aprovechan los mecanismos de reparación del DNA que se activan mediante la generación de roturas del DNA de doble hebra. Estos mecanismos de reparación del DNA pueden insertar o eliminar nucleótidos en la zona de ruptura de la doble hebra e inactivar un gen, o incorporar un nuevo fragmento de DNA dentro de una ruptura de doble hebra para cambiar la función de un gen. ¿Qué propiedades del sistema CRISPR / Cas9 son buenas para la edición de genes? 18. La transferencia lateral de genes (TLG) o transferencia horizontal de genes se re fi ere al movimiento no sexual de material genético entre genomas. T LG se distingue de la herencia vertical, la transmisión de genes de padres a hijos, ya que TLG puede ocurrir entre miembros de diferentes especies y entre células bacterianas y de Arqueas. En procariotas existen tres procesos que median TLG: (1) transmisión viral de DNA entre células (transducción); (2) tomar DNA directamente del medio ambiente (transformación); y (3) transferencia de DNA de una célula a otra a través de una estructura física llamada pilus (conjugación). a) ¿Se puede cortar el DNA recibido por TLG mediante enzimas de restricción? ¿Por qué o por qué no?
- 11. 11 b) ¿Se puede integrar el DNA recibido por TLG en el locus CRISPR? ¿Por qué o por qué no? c) En el espacio a continuación, dibuja los pasos necesarios para que el DNA recibido por transformación se integre en el locus CRISPR.
- 12. 12 Repasa los modelos 1-3 con los siguientes objetivos de aprendizaje para esta actividad en mente. Al final de esta actividad, puedo: 19. Divide los objetivos de aprendizaje anteriores entre los miembros del equipo a) Cada miembro del equipo debe turnarse para describir o explicar el contenido de su objetivo de aprendizaje al resto de su equipo. Dibuja moléculas y estructuras relevantes como ayuda para tu instrucción. b) ¿Cuáles fueron las características más difíciles de describir o explicar de la inmunidad procariota? Enumera estas características desafiantes a continuación. c) ¿Qué métodos fueron más efectivos para describir o explicar la inmunidad procariota? A continuación, enumera estos métodos efectivos. 20.Ahora que has revisado esta actividad, ¿qué preguntas tienes sobre la inmunidad procariota? ¿Cómo puedes encontrar respuestas a estas preguntas? Revisión 1. Describi las funciones de las enzimas de restricción, las secuencias de reconocimiento y las metiltransferasas en la respuesta inmune innata procariota. 2. Explica cómo se registran las infecciones, ocurridas en el pasado, en los loci CRISPR de los genomas procarióticos. 3. Explica cómo los loci CRISPR proporcionan a los procariotas una respuesta inmune adaptativa especí fi ca para un DNA objetivo.
- 13. 13 Reflexión 21. Reflexiona sobre lo bien que trabajaste como equipo durante esta actividad. a) ¿Qué hicieron como equipo que permitió un funcionamiento adecuado? b) ¿Qué podrías mejorar para futuras actividades grupales?
